百迈客微生物多样性APP包含30余项分析内容,自上线以来主流程运行35W+次,个性化运行300W+次,为了丰富分析内容,近期我们会持续对分析内容进行优化更新,我们一起来看看本期的新增内容吧。
1.群落结构分析
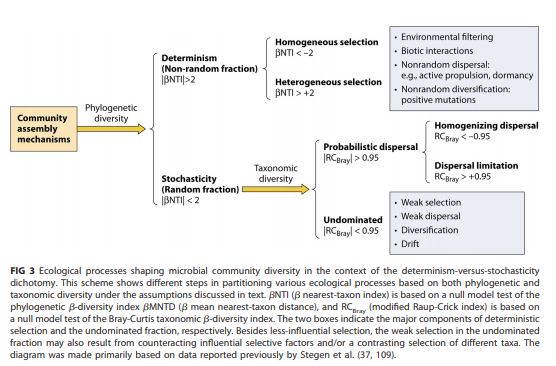
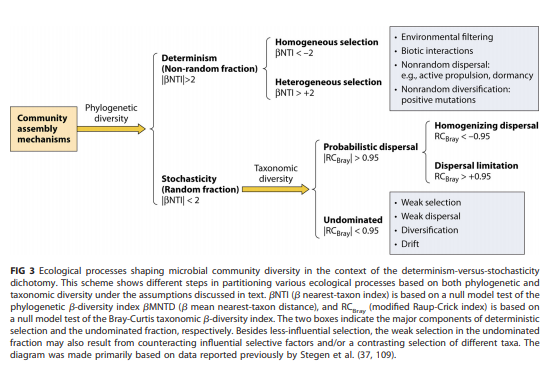
微生物群落生态学的一个主要目标是了解构成跨时空物种丰度模式的过程。确定性和随机性两种类型的过程会影响群落的聚集。确定性过程与生态选择相关,随机过程包括不可预测的扰动、概率性的散布和随机的出生-死亡事件等,这些变化不是由环境决定的适应性结果。通过零模型量化群落的绝对系统发育距离与随机系统发育距离的偏离度,偏离程度越大,群落受确定性因素的影响越大,偏离度越小,群落受随机性因素的影响越大。通常使用βNTI(最近种间亲缘关系指数)以评估不同时空尺度下随机性和确定性过程对微生物群落组装的影响。
云平台上关于群落结构分析的操作非常简单,打开结题报告后点击“Beat多样性分析”中的群落结构分析,选中需要分析的样品点击提交,然后可以在分析记录界面查看分析结果(由于会做999次重复计算,大家耐心等待哦)。
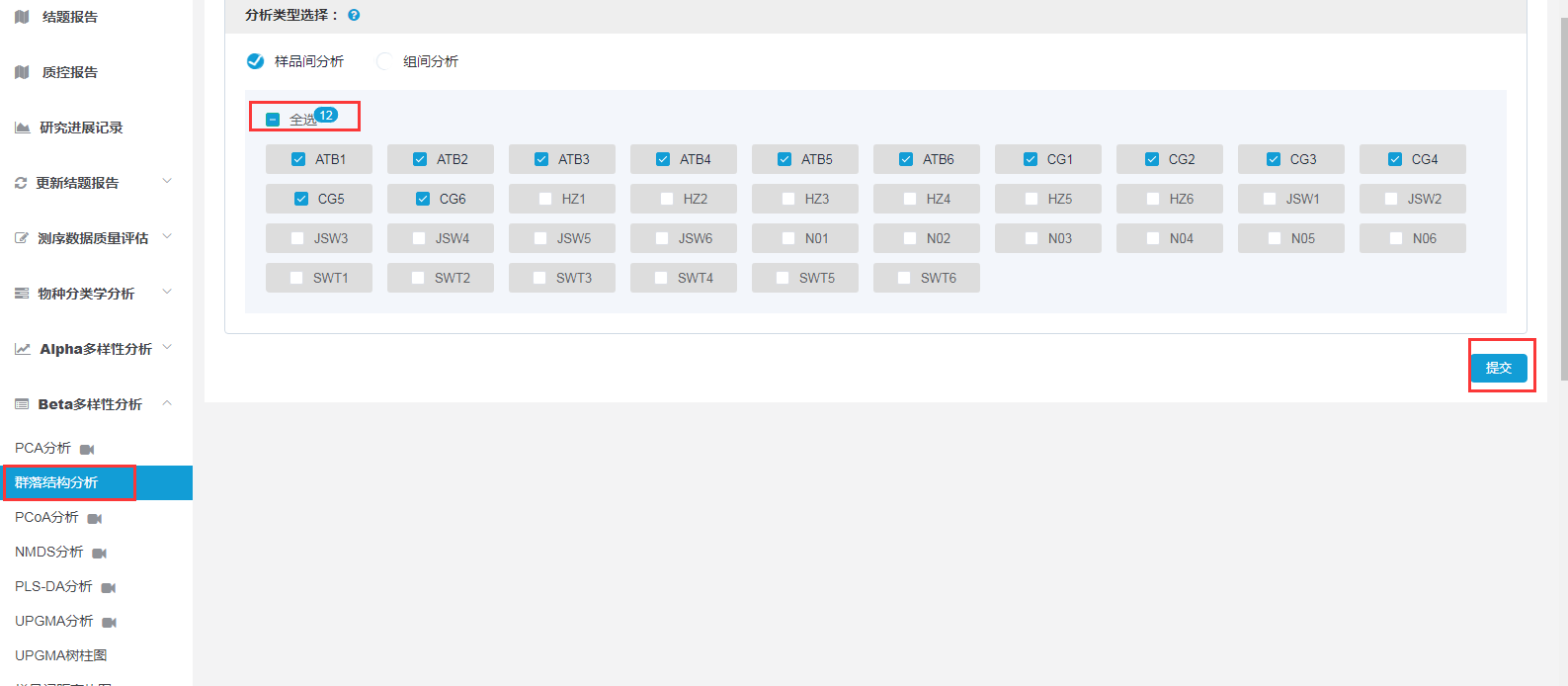
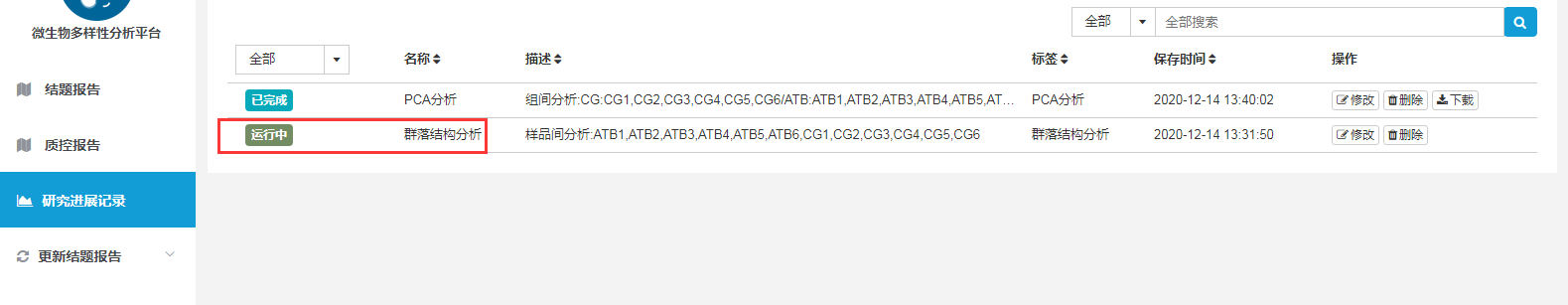 分析结果包含2个表格,分别记录两两样品之间βNTI和RCbray的值。
分析结果包含2个表格,分别记录两两样品之间βNTI和RCbray的值。

其中,| βNTI |>2表示观察到的两个群落之间的更替主要由选择控制,其中βNTI>+2与变量选择一致,而βNTI<-2表示同质选择。因此,| βNTI |<2意味着一组群落的更替受扩散限制、均匀化扩散或未消除过程的控制。为了理清这些过程,Raup-Crick矩阵(RCbray)基于群落的标准Bray-Curtis矩阵构建,提供有关所观察到的流动程度是否明显偏离预期的信息。这个值等于观测到的Bray-Curtis和零分布之间的偏差,范围是-1到+1。| RCbray |<0.95可以解释为终止过程的影响。反过来,扩散限制加上漂移导致大于预期的周转率(RCbray>+0.95),而RCbray<-0.95则表明群落组成的周转率主要受均匀扩散控制。
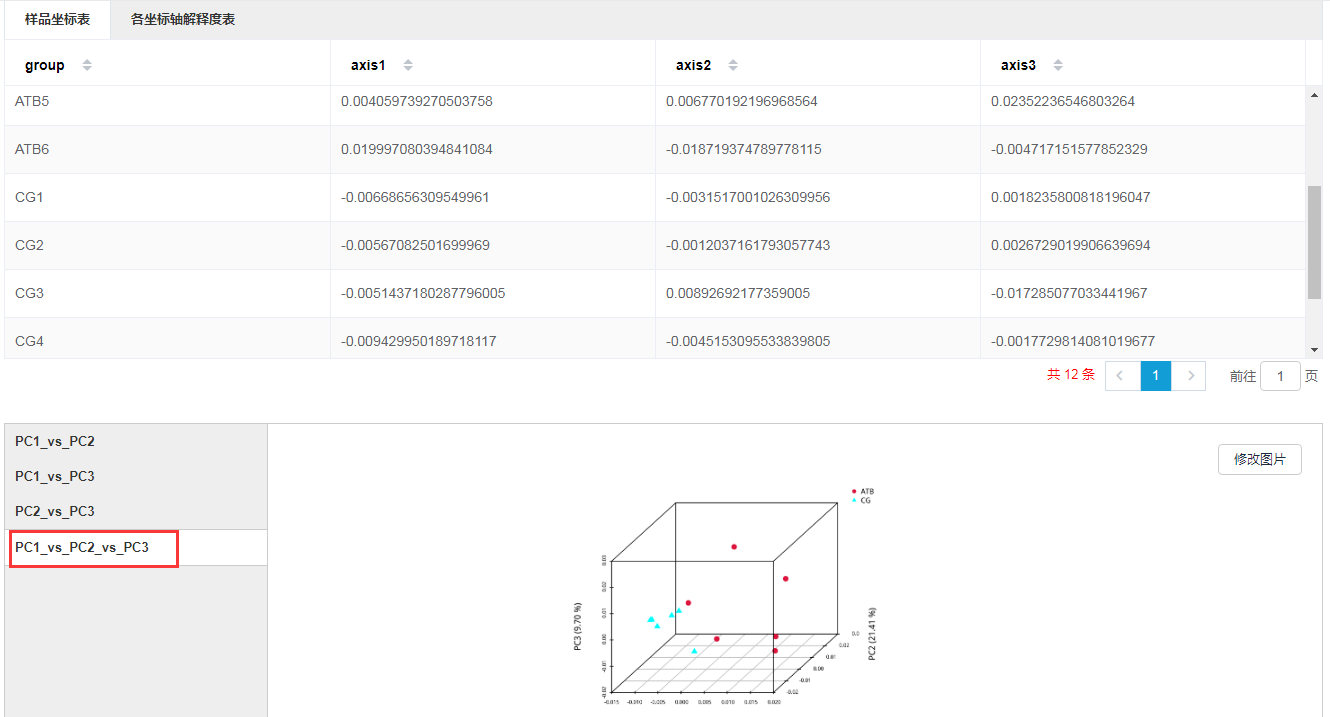
2.三维PCA/PCoA
PCA/PCoA分析通常使用第一轴和第二轴的信息展示样品或者分组之间的聚集和差异,当第一轴和第二轴不足以展示组间差异时,我们可以通过三维图查看前3轴对样品间差异的影响。打开结题报告后点击“Beat多样性分析”中的PCA分析或者PCoA分析,选中样品或者分组,提交任务后会显示三维分析结果。
本期关于新增个性化就介绍到这里了,后续还有picrust2、funguild、tax4Fun2、MicroPITA、相关性分析等多项分析内容正在准备上线中,欢迎大家随时关注!
参考文献:Jizhong, Zhou, Daliang, et al. Stochastic Community Assembly: Does It Matter in Microbial Ecology[J]. Microbiology & Molecular Biology Reviews, 2017.





 京公网安备 11011302003368号
京公网安备 11011302003368号