重测序是对已知基因组序列的物种进行不同个体的基因组测序,并进一步对个体或群体进行差异性分析。那三代重测序又是什么呢?它则是用三代测序技术对已知基因组序列的物种进行不同个体的基因组测序。
三代测序的最主要的特点就是读长长,Nanopore测序的读长甚至能达到Mb级别。下述是三代重测序能做一些分析内容。
【结构变异】
结构变异(SV),指基因组上发生的大片段插入(INS)、缺失(DEL)、倒位(INV)、易位(TX)、重复(DUP)等类型的变异。这里的大片段一般指大于30或50bp的区域。插入、缺失很好理解就是,多了一段或者少了一段;重复就是有一段区域的序列重复出现;倒位就是序列翻转了一下,如本来那个位置该是AATTG的,结果变成了GTTAA;易位的话就是序列位置的变化,又进一步分为染色体内易位和染色体间易位。
据统计,基因组结构变异可能导致的遗传性疾病已经超过1,000种,对于每个人来讲其基因组都有至少20,000个的结构变异,这些变异带来的影响或许比SNVs或InDels带来的影响更大。检测特异的SV能够用于肿瘤分类的基础以及肿瘤严重程度和治疗反映的潜在预后值。
【染色体碎裂】
染色体碎裂即为一个染色体在复制过程被打碎,然后这些碎片以另一种顺序重组(其实小编的理解就是一堆结构变异集中发生了)。
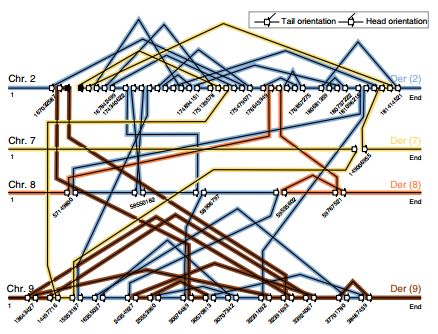
染色体碎裂事件[1]
发生染色体碎裂的细胞一般会死亡,而如果这种细胞存活下来就有可能造成癌症发生。Each coin has two sides,染色体碎裂的发生也并不见得都是坏处,2015年的一篇文章就说明了染色体碎裂的治愈机制所带来的医学奇迹[2]。
【拷贝数变异】
拷贝数变异(CNV),一般指长度为1 kb 以上的基因组大片段的拷贝数增加或者减少,是结构变异中的重要组成部分。而拷贝数是指某基因在某一生物的基因组中的个数。单拷贝就是该基因在该生物基因组中只有一个,多拷贝则指有多个。而像人、鼠其实如果不发生拷贝数变异的话,应该都是二拷贝,一个来自父亲,二另一个来自母亲。之所以要介绍一下拷贝数,是因为小编以前真不太理解,迷之微笑
拷贝数变异则与许多复杂遗传疾病的致病机制或易感性相关,包括肿瘤、获得性免疫缺陷综合征、系统性红斑狼疮、自身免疫炎症疾病、精神分裂症、癫痫、类风湿关节炎、智力迟滞和发育迟滞等。
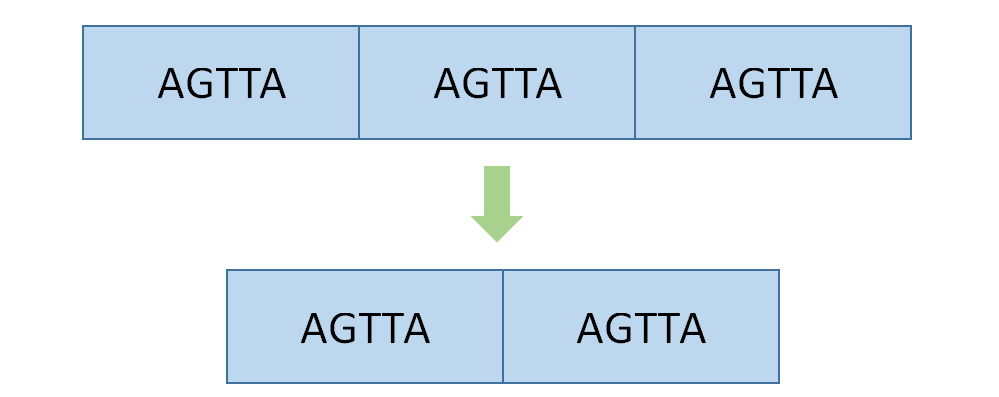
【重复序列变异】
主要指1-6bp 短串联重复序列STR(short tandem repeat)、微卫星不稳定性MSI(microsatellite instability)以及6bp 以上可变串联重复序列VNTR(Variable Number of Tandem Repeats)。小编画个图让大家直观的感受一下,是不是一下子就明白啦!这种重复序列的变异已经发现和40多种神经肌肉和神经退行性疾病相关。
【HLA单倍型】
指一条染色体上HLA各位点基因紧密连锁组成的基因单位。HLA即人类白细胞抗原,是迄今已知基因中等位基因多态性最高的基因复合体,也是不同个体进行器官或组织细胞移植时发生排斥的主要成分。人体细胞是二倍体型,两个单倍型则分别来自父亲和母亲。由于一条染色体上HLA各位点的距离非常近,很少发生同源染色体之间的交换,因此亲本的HLA以单倍型为单位将遗传信息传给子代。
HLA蛋白在免疫回应中起到非常重要的作用,并且涉及到很多人类病理状况包含自身免疫疾病,传染病,癌症和药物反映。临床上,HLA基因序列信息广泛的用于器官移植,以鉴定匹配的供体和受体HLA等位基因。匹配上正确的HLA 型别对骨髓移植(白血病等)和器官移植能否成功起到决定性的作用,高度相似的等位可以改善器官移植的结果并降低排斥的风险。
其实说实话,上述分析内容二代测序都能做,但二代测序由于其短读长对于这些分析内容不具有检测优势!结构变异的检测需要检测到断点,而二代的短read有可能检测不到,而即使检测到的那些也存在很高的错误率。三代测序直接就能测到包含结构变异的序列,无需进行组装。真的是天然的优势啊!
参考文献
[1]Cretu Stancu M , Van Roosmalen M J , Renkens I , et al. Mapping and phasing of structural variation in patient genomes using nanopore sequencing[J]. Nature Communications, 2017, 8(1):1326.
[2]McDermott DH, Gao JL, Liu Q, et al. Chromothriptic cure of WHIM syndrome. Cell 2015; 160:686-99.






 京公网安备 11011302003368号
京公网安备 11011302003368号