 近日, Microbiology Spectrum(IF 9.0431)在线发表了广东省农科院作物所黄立飞副研究员、房伯平研究员为通讯作者的研究论文 “Whole-Genome Sequencing and Comparative Genome Analysis of Fusarium solani-melongenae Causing Fusarium Root and Stem Rot in Sweetpotatoes”,该研究报道了F. solani-melongenae 分离株 CRI 24-3 的全基因组组装序列,并且深入探讨其功能基因信息,为其他密切相关的镰刀菌属物种的基因组研究提供基础,通过比较基因组分析促进了对镰刀菌基因组特征和进化关系的整体理解。百迈客有幸参与此项研究工作,对该真菌全基因组进行测序组装注释和比较基因组分析。
近日, Microbiology Spectrum(IF 9.0431)在线发表了广东省农科院作物所黄立飞副研究员、房伯平研究员为通讯作者的研究论文 “Whole-Genome Sequencing and Comparative Genome Analysis of Fusarium solani-melongenae Causing Fusarium Root and Stem Rot in Sweetpotatoes”,该研究报道了F. solani-melongenae 分离株 CRI 24-3 的全基因组组装序列,并且深入探讨其功能基因信息,为其他密切相关的镰刀菌属物种的基因组研究提供基础,通过比较基因组分析促进了对镰刀菌基因组特征和进化关系的整体理解。百迈客有幸参与此项研究工作,对该真菌全基因组进行测序组装注释和比较基因组分析。摘要
甘薯(Ipomoea batatas)是全球第八大重要作物,然而,甘薯的生产和质量受到世界各地流行的镰刀菌病害的威胁。在这项研究中,研究了一种导致甘薯根和茎腐烂的镰刀菌。使用二代和三代高通量测序技术分离和测序病原真菌 CRI 24-3,获得包含 15,374 个预测编码基因的 49.6 Mb 基因组。分子系统发育分析表明,CRI 24-3 是 F. solani-melongenae 菌株,位于 F. solani 物种复合体 (FSSC) 的进化枝 3 内。与其他测序 FSSC 中鉴定的毒力因子数量相比,CRI 24-3 显示出相对较高数量的毒力因子,例如碳水化合物活性酶 (CAZymes)、病原体-宿主相互作用 (PHI) 蛋白和萜烯合酶 (TSs)成员。比较基因组分析揭示了 CRI 24-3 与其他 FSSC 物种之间相当大的保守性和独特性。总之,本研究的结果提供了有关甘薯镰刀菌的重要遗传信息,有助于探索致病机制和制定镰刀菌病管理策略。
结 果
真菌分离和形态学分析表明CRI 24-3是FRST的病原菌
田间分析表明,水浸病斑最初出现在FRST感染甘薯的基部茎上(图1A)。此外,在潮湿或多雨的天气中,观察到大量的红色外皮覆盖在坏死的基部茎上(图1B)。随着病害蔓延,上部茎叶逐渐褪绿和枯萎。贮藏根呈凹形病斑,环状边缘清晰,白色菌丝分布在凹陷病斑上,块茎内部有破裂的坏死组织(图1C和D),从而显着降低甘薯的产量和质量。从患病甘薯样品中分离出优势真菌菌落 CRI 24-3。然后根据 Koch 的假设进行 CRI 24-3 的致病性测试。切片的根部观察到超过接种点的水褐色病斑,菌丝稀疏,阴性对照不存在(图1C),表明CRI 24-3是甘薯FRST的致病因子。

图 1 大田感染 FRST 的甘薯植株表型。 (A)受感染的茎和叶。(B)覆盖基部茎的带红色外皮。(C和D)受感染的贮藏根。(E)在致病性测试中接种 CRI 24-3 (右) 和阴性对照 (左) 的贮藏根。标尺 = 5 厘米。
CRI 24-3 在马铃薯蔗糖琼脂 (PSA) 和合成低营养琼脂 (SNA) 上培养,用于进一步的形态学分析。在培养箱(25°C、12 小时光周期和 75% 相对湿度)中培养 4 天后,PDA 上的平均菌落直径为 4.4 cm。蓬松的菌落有分隔的气生菌丝体,散布在盘子上。菌落表面呈乳白色,背面呈黄色(图2A至C)。小分生孢子丰富,呈椭圆形至肾形,大多数为 1 隔(图 2E)。1 隔小分生孢子为 (7.8 至 13.8) × (2.1 至 3.9) μm。大分生孢子呈镰刀形,3-5 纵隔,顶端细胞稍弯曲,基底细胞呈足状(图2F)。3 至 5 隔大分生孢子的平均宽度为 4.1 至 4.9 μm。来自短侧枝的末端或闰厚厚孢子(6.1至7.4μm)是球形和粗糙的(图2H)。4周后,菌落被点状暗红色外皮覆盖,类似于田间受感染的甘薯(图1B和2I)。CRI 24-3 的梨形外皮层具有乳头状颈部和小孔(图 2J),子囊孢子通过小孔释放。此外,棒状子囊含有 8 个单列 1 隔子囊孢子,大小为(10.7 至 12.6)×(3.9 至 5.0)μm(图 2K和L)。相比之下,SNA 上的菌落生长较弱(图 S1),底物菌丝稀疏,4 天后平均直径为 4.1 厘米。SNA上CRI 24-3分生孢子和周壳的数量相对于PSA上的较少。然而,分生孢子和外皮的形态特征与在 PDA 上观察到的相似。分离株CRI 24-3(登录号ACCC 39784)的代表性培养物保藏在中国农业培养物保藏中心。
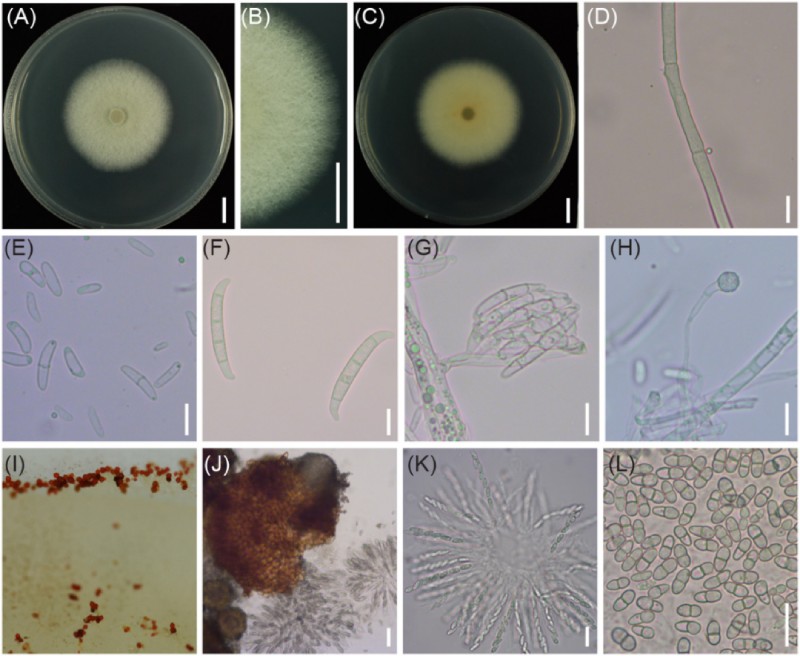
图2 CRI 24-3在PSA上的形态特征。 (A 到 C) 培养 4 天后从表面和背面的菌落。标尺 = 1 厘米。(D) 气生菌丝。(E) 小分生孢子。(F) 大分生孢子。(G) 假头中的分生孢子。(H) 衣藻。标尺 = 10 微米。(I)Perithecia。(J) 放大的外皮层。标尺 = 50 微米。(K) 子囊轴承 (L) 八个子囊孢子。标尺 = 20 微米。
生成并注释了 CRI 24-3 的高质量基因组组装草图
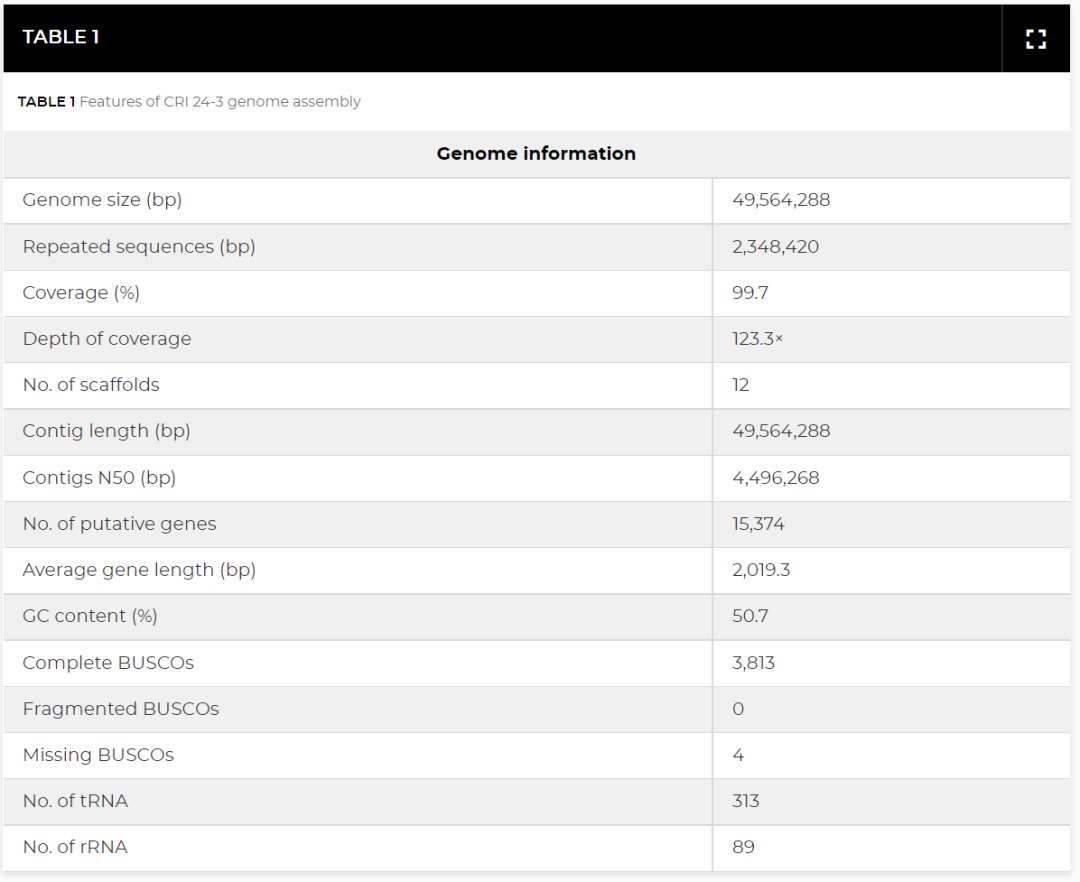
经数据质控后共获得 452,011 条高质量的clean reads(平均长度 13,525.1 bp)(表 S1)。CRI 24-3的 49.6 Mb 基因组是由 12 个contigs产生的,该基因组具有 4.5 Mb 的contigs N50 和 50.7% 的 GC 含量,覆盖深度估计为 123.3 倍(图 3;表 1)。基因组质量评估结果表明,CRI 24-3 的基因组组装完整且准确,因为 CRI 24-3 中的单拷贝直系同源基因与 sordariomycetes_odb10 数据集中所有 3,817 个完整核心基因的 99.9% 匹配(表 1)。
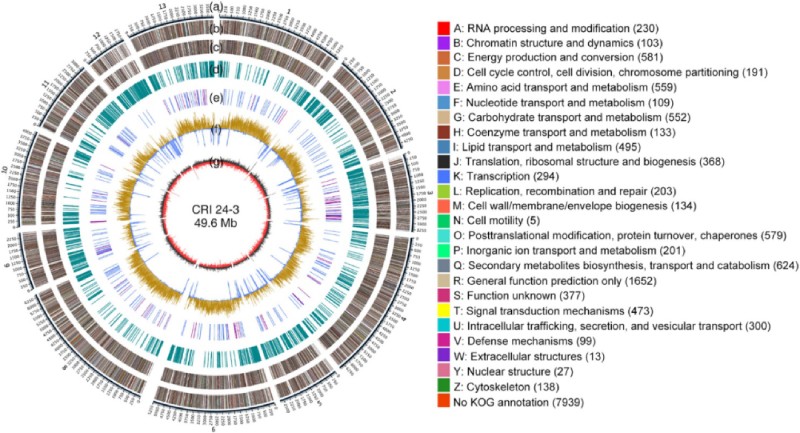
图 3 CRI 24-3 基因组组装圈图。 (A) 12 个contigs的物理位置。标尺 = 1 kb。(B 和 C)具有 KOG 类的正向和反向链上的蛋白质编码基因。(D) 重复序列。(E) 正向链上的 tRNA(蓝色)和 rRNA(紫色)编码基因。(F) 某些区域的 GC 含量高于(黄色)或低于(蓝色)平均基因组 GC 含量。(G) GC-skew = (G−C)/(G+C),具有正(黑色)或负(红色)值。
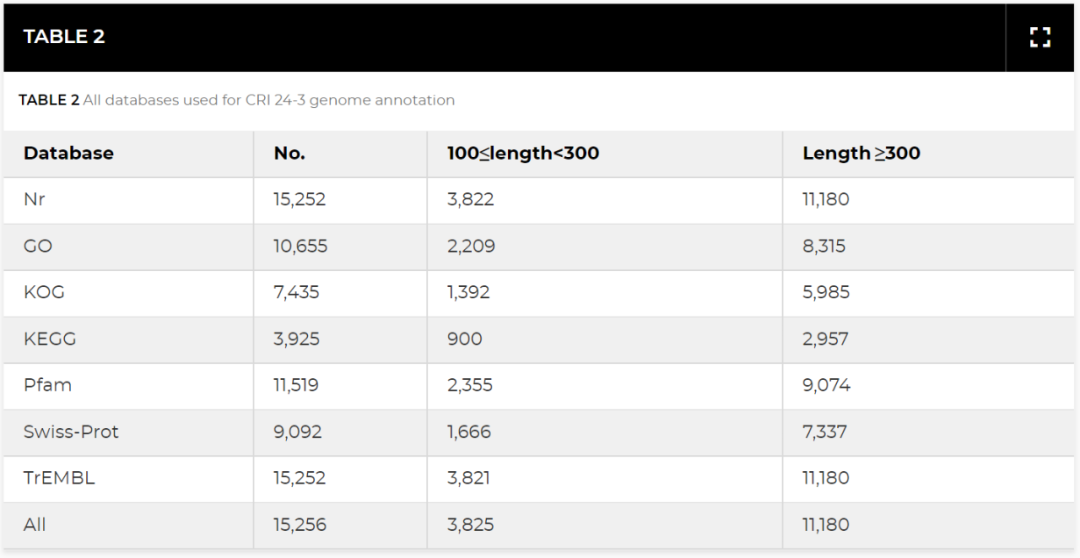
使用三种基因结构预测方法,共鉴定了 15,374 个平均基因长度为 2.0 kb 的预测基因(图 S2A;表 1)。此外,基于序列相似性比较,通过多个功能数据库注释了 15,256 个蛋白质编码基因(表 2)。基于非冗余蛋白质序列 (Nr) 数据库分析(图 S2B),CRI 24-3 中约 80.3% 的蛋白质编码基因与F. vanettenii 77-13-4 的基因组匹配,这表明这两个物种密切相关。此外,对 10,655 个蛋白质编码基因进行了基因本体论 (GO) 分析(表 2) 并在功能上分为三类:“细胞成分”(7,100)、“分子功能”(8,279) 和“生物过程”(8,069)。使用真核直系同源群 (KOG) 数据库进行的进一步功能分析表明,“仅一般功能预测”类别 (R, 22.2%) 的蛋白质数量多,其次是“次级代谢物生物合成、转运和分解代谢”类别(Q,8.4%)和“能源生产和转换”类别(C,7.8%)(图 3)。此外,使用京都基因和基因组百科全书(KEGG)数据库对 3,925 个编码基因的分析表明,2,329 个基因富集在属于五个类别的 114 个代谢途径中(图 S4;表 2)。大多数基因富含碳水化合物(471)和氨基酸代谢(435)途径。
基于分子系统发育分析,CRI 24-3 被鉴定为F. solani-melongenae
使用 BLASTn 工具与 NCBI 数据库的比对表明,从 CRI 24-3 基因组 DNA 扩增的 ITS 序列 PCR 与F. solani-melongenae NRRL 22101 具有 99.8% 的同一性,具有 100% 的查询覆盖率(未发表的数据),表明 CRI 24-3 是 FSSC 的成员。为了更准确地识别 CRI 24-3,进行了基于ITS、RPB2和TEF 1-α的串联序列的信息系统发育分析(图 4A)。组合序列树中的大多数引导值高于 ITS 树(未发布数据)中的值。三基因座树显示了一个优势分支,包括 FSSC 进化枝 3 内的 38 个群内末端,FSSC 进化枝 1 和 2 内的分类群形成了一个基础姊妹群(图 4A和表 S2)。由 FSSC 分类群形成的主要分支被分成一个末端节点,包括 CRI 24-3 和另一个包含F. protoensiforme (FSSC 32) 和F. riograndense的亚基底节点。重要的是,CRI 24-3 与F. solani-melongenae密切相关,并聚集在 FSSC 进化枝 3 中。因此,FRST 的分离株 CRI 24-3 被鉴定为F. solani-melongenae (FSSC 21) ,此方法是基于 Nilsson 等人提出的方法。
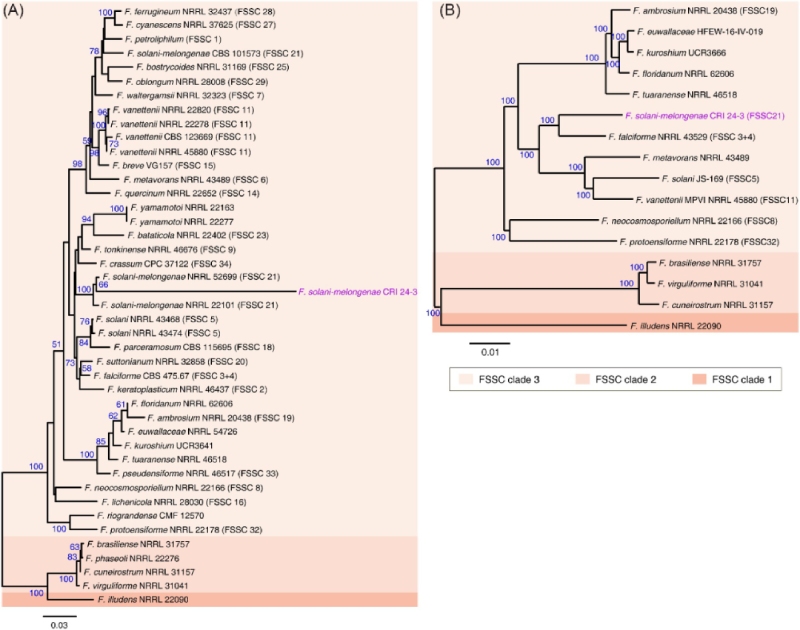
图 4 CRI 24-3 和其他植物病原镰刀菌的系统发育分析。 从 (A) ITS、RPB2 和 TEF 1-α 的串联序列和 (B) 由 16 个 FSSC 物种共享的 1,544 个单拷贝同源基因的组合序列推断出的 ML 树。 引导值(蓝色)表示相关菌株聚集在一起的分支百分比。 括号中的阿拉伯数字区分了 FSSC 进化枝 3 中系统发育不同的物种。
探索了 CRI 24-3 和 15 个基因组测序的 FSSC 物种之间的系统发育关系(表 S3)。F. illudens NRRL 22090 被用作外群以生成有根的系统发育树。来自 16 个镰刀菌基因组共享的 1,544 个单拷贝同源基因的全基因组系统谱得到了很好的支持,其中 14 个节点具有 100% 的引导值(图 4B)。16 个 FSSC 物种分为三个已知的进化枝。系统基因组关系分析显示 CRI 24-3 与F. falciforme (FSSC 3 + 4)密切相关,具有 100% 引导支持。这两个物种与F. vanettenii、F. solani和F. metavorans形成了一个单系群。,表明这些物种可能共享一个祖先。
在 CRI 24-3 中发现了丰富的毒力因子,包括独特的单孢二烯合酶
在这项研究中,在 CRI 24-3 中鉴定了 889 个推定的 CAZymes 编码基因(表 S4),这可能与前面描述的突出的碳水化合物代谢途径有关(图 3;图 S4)。CRI 24-3 中 CAZymes 的数量相对于其他一些镰刀菌更高(例如, FSSC 进化枝 2 内的F. virguliforme中的 629 个;FSSC 进化枝 3 内的F. neocosmosporiellum 中的551个;在来自 F. sambucinum 物种复合体的禾谷镰刀菌中的481个)。CAZymes 根据它们的家族分布和基因数不同(图 5A )分为六类,糖苷水解酶 (GHs, 379) 是大的一类,其次是碳水化合物酯酶 (CEs, 199) 和辅助活性 (AAs, 136)。CRI 24-3 有 60 个 GH 家族,其中大多数酶分布在 GH3 (37)、GH43 (35)、GH109 (35) 中,而一些常见的 GH 亚家族,如 GH29、GH30 和 GH44,在 CRI 24-3中不存在(图 5B ),类似于F. virguliforme 中的 CAZyme 曲线。在 CRI 24-3 中鉴定了来自 GH11 的三种假设的 β-1,4-木聚糖酶,称为 FsmGH11.1、FsmGH11.2 和 FsmGH11.3(表 S4)。多重比对(图S5)显示FsmGH11.3与NhGH11(GenBank登录号XP_003050975.1 )具有高的序列相似性(44.1%),NhGH11是来自F. vanettenii GH11的β-1,4-木聚糖酶被证明可以分解各种木聚糖底物,这暗示 FsmGH11.3 和 NhGH11 可能具有相似的木聚糖酶水解能力。
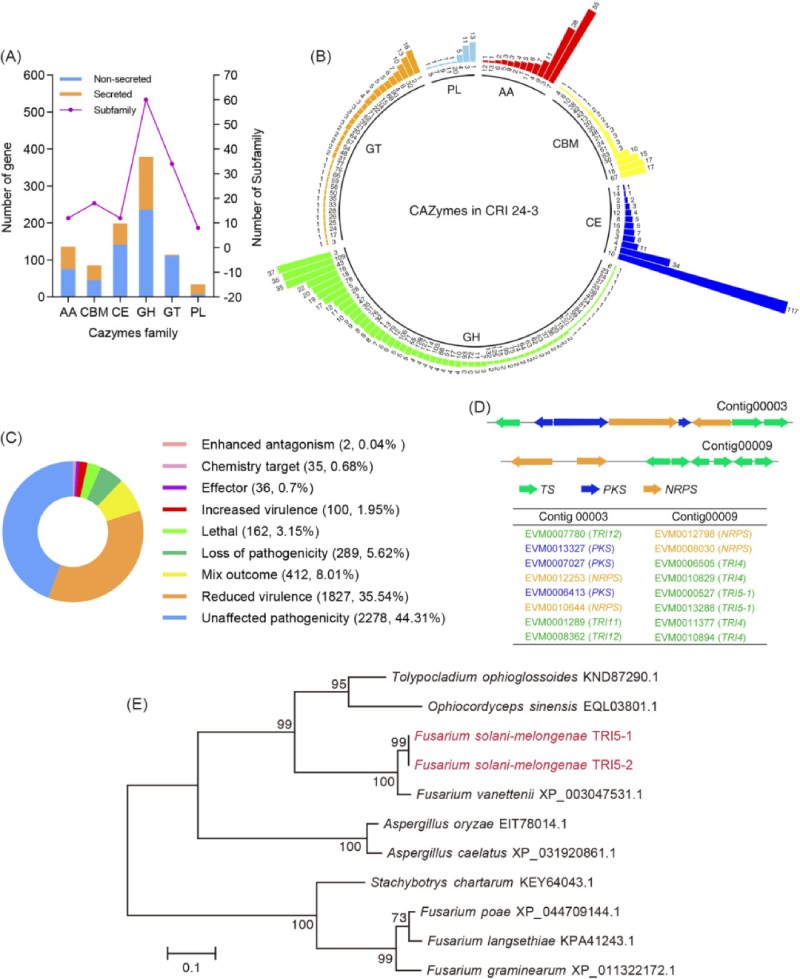
图 5 CRI 24-3 蛋白质组中的 CAZymes 和 PHI 蛋白。 (A) CAZymes 及其相关家族的数量。 (B) CAZymes 家族分布。 内圈附近和条形顶部的数字分别代表家族 ID 和蛋白质的数量。AA:辅助活性,CBM:碳水化合物结合模块,CE:碳水化合物酯酶,GH:糖苷水解酶,GT:糖基转移酶,PL:多糖裂解酶。 (C) 5141 PHI 蛋白的功能。 混合结果表明在一种蛋白质中观察到至少两种不同的功能。 (D) 编码 PKS、NRPS 和 TS 的串联阵列基因聚集在 CRI 24-3 组装的 Contig00003 和 Contig00009 中。 (E) 从 CRI 24-3 和其他相关物种的 11 条单孢菌素合酶序列推断的系统发育关系分析。
比较基因组分析揭示了 CRI 24-3 和其他 FSSC 物种的基因组保守性和独特性
比较来自 18 个镰刀菌属物种的基因组,包括 16 个已测序的 FSSC 物种、F. fujikuroi和F. oxysporum,以进一步探索基因组多样性和进化关系(表 3;表 S3)。通过基因家族结构分析,共鉴定和注释了包含 279,680 个基因的 16,130 个家族(GF1 至 GF16,130)。结果表明,18个类群共有4300个基本科,其次是两个类群的2990个科和786个物种特异性科(图6A和B ))。大约 59.6% 的检测到的基因属于共享家族,其中 1,544 个家族具有单拷贝基因。值得注意的是,上一部分提到的效应子PKS(EVM0010851.1)聚集在一个共享家族(GF2338)中,在Pfam注释中具有特征性的酰基转移酶结构域。
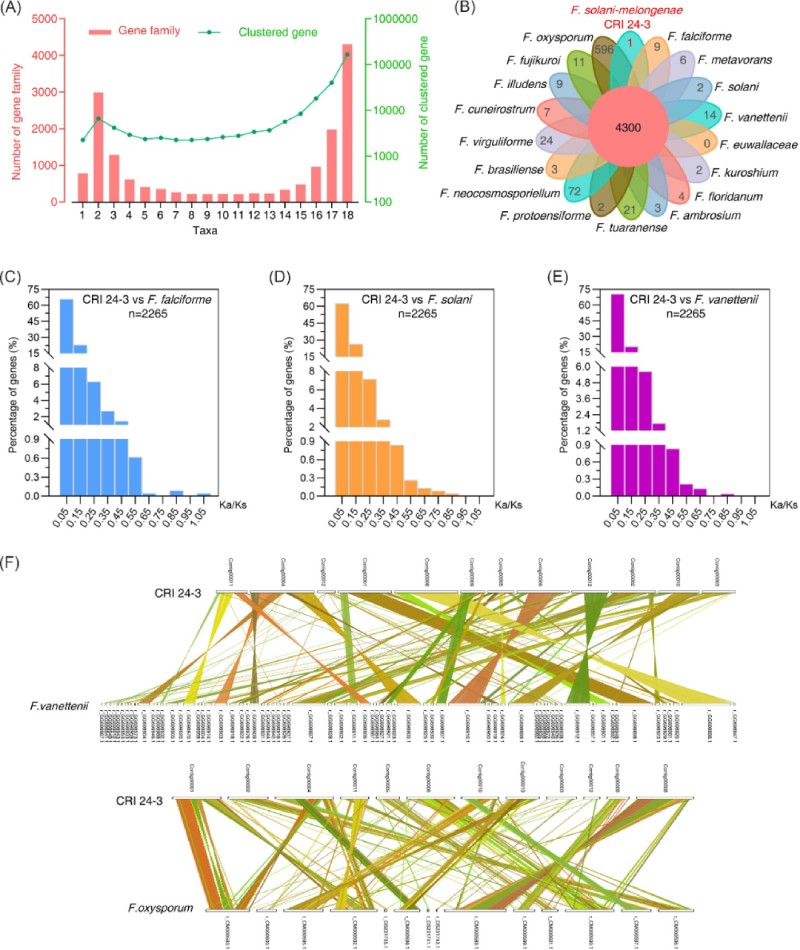
图6 CRI 24-3与其他镰刀菌的基因组比较分析。 (A)基因家族和聚集在相应家族中的基因数量从1到18不等。(B)花形维恩图。 中心值表示 18 个镰刀菌属中所有共有基因家族的数量; 花瓣的值表示每个物种中特有基因家族的数量。 (C 到 E)CRI 24-3 和 F. falciforme、F. solani、F. vanettenii 之间基因对的 Ka/Ks 比率分布。 小写字母“n”后面的值表示所有检测到的基因对的数量。 (F) 显示基因组共线性的双同线性图。 不同颜色的线用于连接 CRI 24-3 和 F. vanettenii (顶部) 或 F. oxysporum (底部) 之间的直系同源基因对。
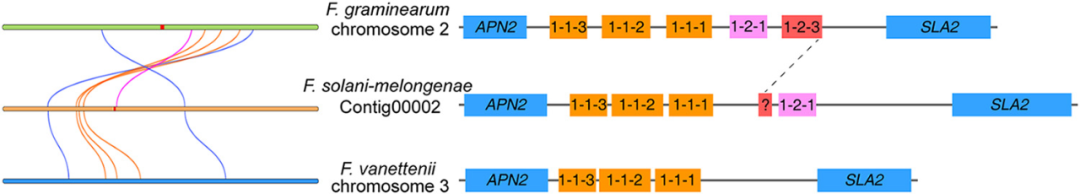
其他三种密切相关的 FSSC 物种F. falciforme、F. solani和F. vanettenii的基因组被用作参考基因组来探索 CRI 24-3 的选择压力。分别确定了 CRI 24-3 与 F. falciforme、F. solani 和F. vanettenii 之间的 2265、2272 和 2272 直系同源物对的非同义替换率 (Ka) 与同义替换率 (Ks) 的比率( 图 6C 至 E)。Ka /Ks总体分析的值小于 1,表明 CRI 24-3 中的大多数直系同源物似乎都经过了纯化选择并且高度保守。然而,CRI 24-3 和F. falciforme基因组的比较确定了一个快速进化基因对(EVM0014458.1 与 GE10416_g)的 Ka /Ks比率大于 1,表明阳性选择可能发生在进化。基因组共线性分析表明,F. vanettenii和F. oxysporum基因组中的几个染色体片段在 CRI 24-3 中浓缩成一个片段,并有一些倒位(图 6F )。此外,CRI 24-3 中的一些直系同源物具有多对一的关系。CRI 24-3 中至少有两个查询基因与参考物种中的相同直系同源物匹配。值得注意的是,CRI 24-3 的重要基因组区域不能与尖孢镰刀菌基因组中的那些共线性耦合,由 35.9% 的共线性率(共线直系同源物对与所有直系同源物对的比率)支持,该比率低于CRI 24-3 和F. vanettenii (77.6%)。结果表明,CRI 24-3在系统发育上与尖孢镰刀菌相距较远。MAT基因座对于在镰刀菌属中产生子囊孢子至关重要。在此,交配型结构组织 ( MAT ) 基因座在基于简化的共线性分析比较了茄科镰孢菌CRI 24-3、禾谷镰刀菌PH-1 和F. vanettenii 77-13-4(图 7)。与仅携带 MAT1-1 基因的 F. vanettenii 77-13-4相比, CRI 24-3 含有MAT1-1和MAT1-2独特型基因,在单个MAT基因座处与禾谷镰刀菌密切相关,除了 CRI 24-3 是 MAT1-2-3 缺陷型。只有位于 CRI 24-3 中 MAT1-2-1 上游区域的没有任何特征功能域的片段与禾谷镰刀菌中的 MAT1-2-3 具有序列相似性。
总 结
本研究发现了一种新型镰刀菌病害,可导致甘薯根和茎腐烂。致病因子F. solani-melongenae分离株 CRI 24-3 的基因组测序。该结果将指导其他密切相关的镰刀菌基因组序列的组装。对已测序的 FSSC 成员的基因组进行全面的基因组比较分析,可以提高对 FSSC 甚至整个属的遗传特征的理解。此外,进一步分析促进植物感染的毒力因素将为制定镰刀菌病害管理策略提供基础,从而大限度地减少经济损失。
百迈客能提供二代微生物多样性,宏基因组,微生物基因组测序,还拥有PacBio全长微生物多样性,Nanopore宏基因组产品,另外还有微生物绝对定量产品,针对微生物进行精准定量,能多维度满足老师的测序要求。同时,还拥有强大云分析平台,58项标准分析+79项不限次个性化分析随心选择,极大丰富文章图表,满足您的文章需求。如果您对我们的服务感兴趣,欢迎点击下方按钮联系我们。







 京公网安备 11011302003368号
京公网安备 11011302003368号