全长比较转录组
全长比较转录组(Phylotranscriptome)
基于转录组测序的全长比较转录组是通过对同一科、属内不同物种,尤其是复杂的或者无参考基因组的物种,提取mRNA后进行PacBio三代测序,从基因序列水平研究起源于共同祖先的不同物种间的系统发育关系以及分化时间等进化事件;同时挖掘明显受到正向选择或者负向选择的基因,从而快速、全面地揭示选择和适应机制。通过二代测序对三代序列进行校正后,不需要组装即得到了高质量的全长转录本,从而避免了由于拼接引入的错误,分析更精准。
三代全长比较转录组的特点
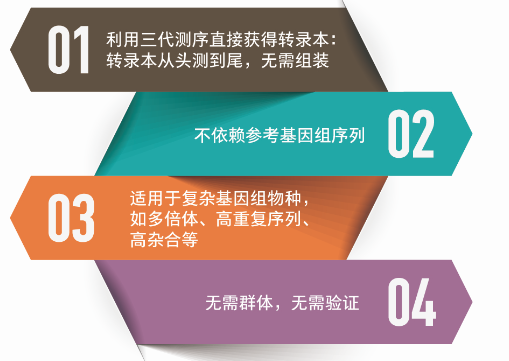
二代与三代转录组完整性比较
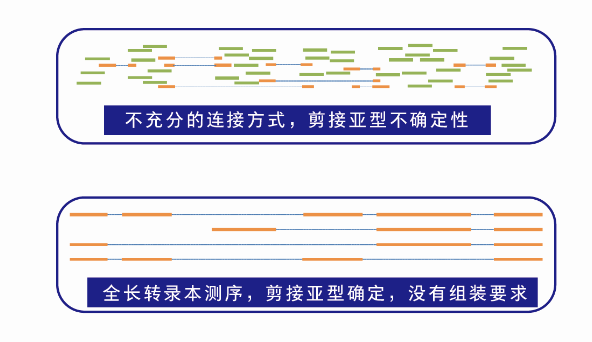
材料选择
有共同祖先的科、属内不同物种
每科属内典型材料1-2个即可
每个个体不同组织样品混合,保证mRNA来源的全面性,获得尽可能多的转录本。
文库构建
二代测序:二代转录组小片段文库。
三代测序:1-2K;2-3K;>3K。
样品要求
三代测序要求:
样品类型:总RNA、组织样;
样品浓度:总RNA浓度≥300 ng/ul;
样品体积:> 10 ul;
样品总量:总RNA用量> 3 ug ;
样品纯度:OD260/280为7~2.5,OD260/230为0.5~2.5,260nm处有正常峰值;
RNA完整性:总RNA的非植物RIN值≥8.0,植物RIN值≥7.5;28S/18S≥1.3;图谱基线无上抬;5S峰正常。
二代测序要求:
总RNA电泳28s和18s条带清晰,且28s亮度大于18s的两倍,5s条带亮度越弱越好。
样品浓度:≥40 ng/μl(Qubit检测)
样品总量:≥3μg(Qubit检测)
样品体积:≥10μl
样品纯度:OD260/280为7~2.5,OD260/230为0.5~2.5
RNA完整性:植物RIN值≥5,非植物RIN值≥7.0;28S/18S≥1;图谱基线无上抬;5s峰较低。
成功案例
全长转录组数据
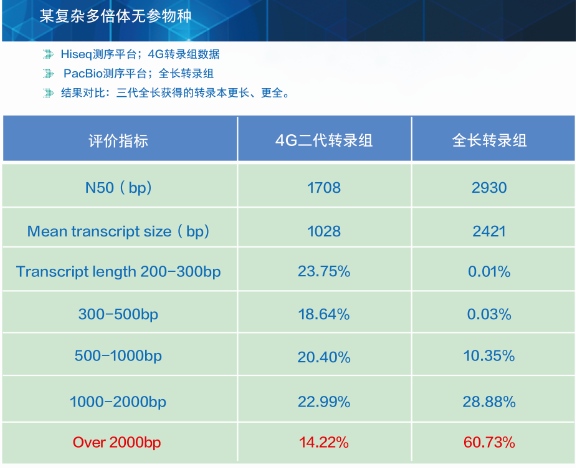
某复杂多倍体无参物种:
Hiseq测序平台;4G转录组数据
PacBio测序平台;全长转录组
结果对比:三代全长获得的转录本更长、更全。
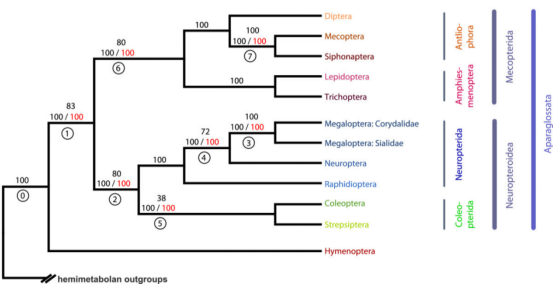
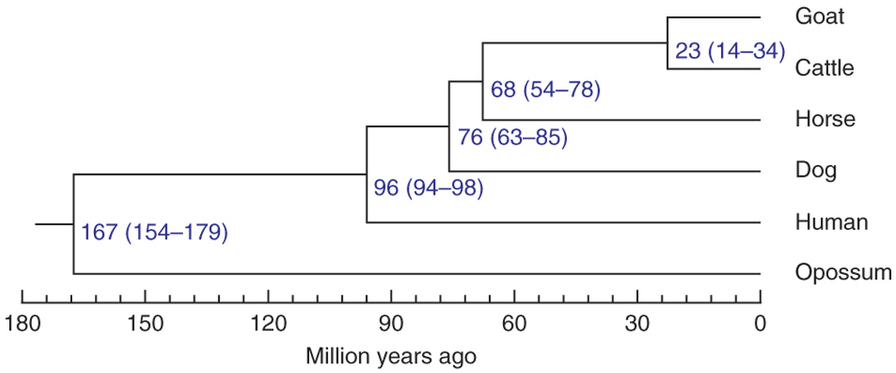
系统发育树
用muscle软件将获得的每个直系同源基因的氨基酸序列进行比对,然后将所有直系同源基因的比对结果合并,使用jModelTest 2软件进行模型选择,根据模型选择结果,用PhyML软件进行似然树的构建,获得各个种间的系统进化树。
分化时间估算
构建进化树后,如有外群和化石标定时间,可以用PAML软件的mcmctree方法计算各个物种的分化时间。如无法提供外群和化石标定时间,可以根据T=Ks/2r估计两两物种的分化时间,其中r为中性突变率,可以查阅相关文献确定。
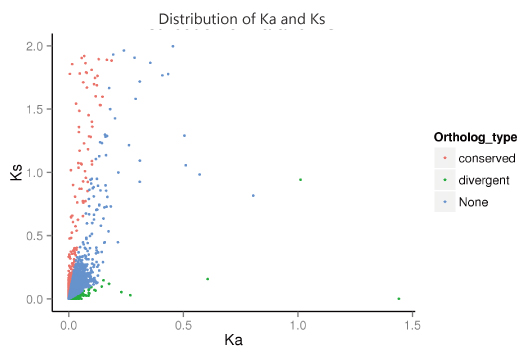
基于Ka/Ks的选择压力分析
Ka/Ks或者dN/dS表示的是非同义突变频率(Ka)和同义突变频率(Ks)之间的比例。一般认为,同义突变不受自然选择,而非同义突变则受到自然选择作用。通过比较非同义替换率和同义替换率的相对比值可以确定这个基因在进化中受到的选择压力,即判断是否有选择压力作用于这个蛋白质编码基因。
1、从基因水平来开展对某(些)物种的研究是最直接、最有效、最易操作的途径,而通过转录组测序是获得基因的最为成熟的手段;
2、对于不同物种,尤其是无参考基因组或参考基因组不完善的同一科属内不同种的进化地位的确定,可通过直系同源基因来实现;
3、对于基因组很复杂,或者同一科属内物种差别大,无法通过重测序进行分析;
4、无需构建群体,研究对象为单独的物种。
2代数据主要是对3代数据进行纠错,从而可以获得更多有效的3代数据,来进行全长转录本的分析;另外,二代转录组数据还可以通过表达量的差异用于验证那些受到正选择的基因。
目前依赖二代的转录组数据进行比较转录组分析的文献有很多,如草莓,番茄,昆虫等,早期发表文章IF比较高,例如番茄(2013 PANS),昆虫(2014 Science),而全长比较转录组分析作为一种新技术去解析物种间进化关系,除了自身的准确性及优势外,作为新技术更容易协助研究者发高层次文章,目前利用全长比较转录组发表的文章几乎没有;另外,全长比较转录组无需实验验证,可快速产出文章。
(1)不同物种,多拷贝基因难以确定基因的一 一对应关系无法比较表达量;当然,单拷贝同源基因可以确定一一对应关系,但是;
(2)表达谱差异分析(例如 RPKM值比较)实际上使用的内参是 RNA总量。相同物种RNA总量稳定,所以没有问题。但不同物种RNA总量未必相同,所以物种间的差异分析就失去了稳定的内参。因此强行比较的话,是不严谨的。
- 广东省农科院联合华南农大、中国热带农科院在荔枝资源群体遗传和果实性状形成方面取得重要进展近日,广东省农业科学院果树研究所荔枝种质资源与育种团队联合华南农业大学园艺学院夏瑞教授团队和中国热带农业科学院 […]阅读更多





 京公网安备 11011302003368号
京公网安备 11011302003368号