Pore-C技术
产品简介
Pore-C是指将染色质构象捕获技术与Nanopore长读长测序技术结合,无需扩增直接检测多向染色质交互信息的一种新技术。该技术除了像Hi-C一样能确定成对基因组结构,还可以直接测量细胞内同时相互作用的多个DNA区域互作信息(higher-order)。
Pore-C技术原理
通过甲醛将基因组DNA与组蛋白交联,保持相互作用位点的空间邻近性。邻近连接后进行限制性酶切。将交联、相互作用的片段连在一起,这些片段经过大小选择和文库制备后基于Nanopore测序平台进行长片段测序。
Pore-C reads与参考基因组比对,以标识单独的对齐;筛选每个比对序列,保留横跨大部分序列的最小片段合集。通过参考序列模拟酶切,将每个序列部分指定到一个限制性片段。将与Pore-C序列相关联的对齐集称为多向(multi-way)连接,并将与连接关联的片段数作为其顺序。
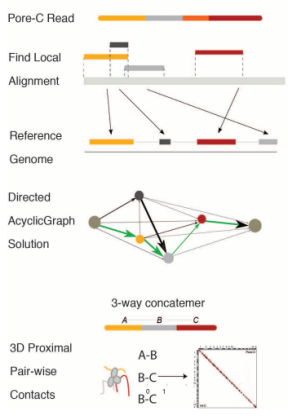
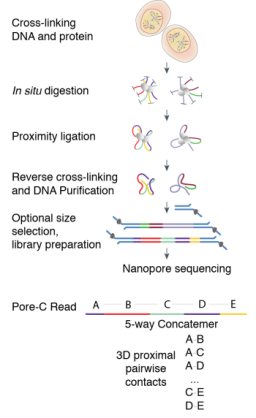
Pore-C技术特点
应用方向
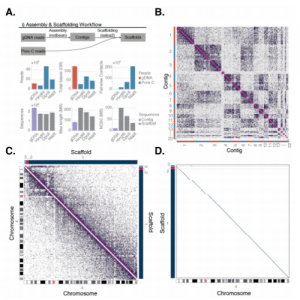
Pore-C辅助基因组组装优势
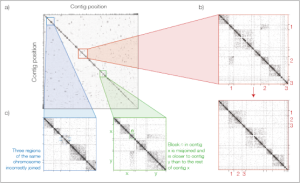
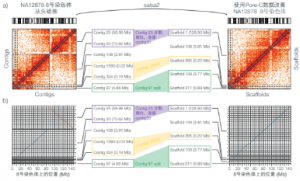
百迈客PoreC技术优势
案例展示
案例一、
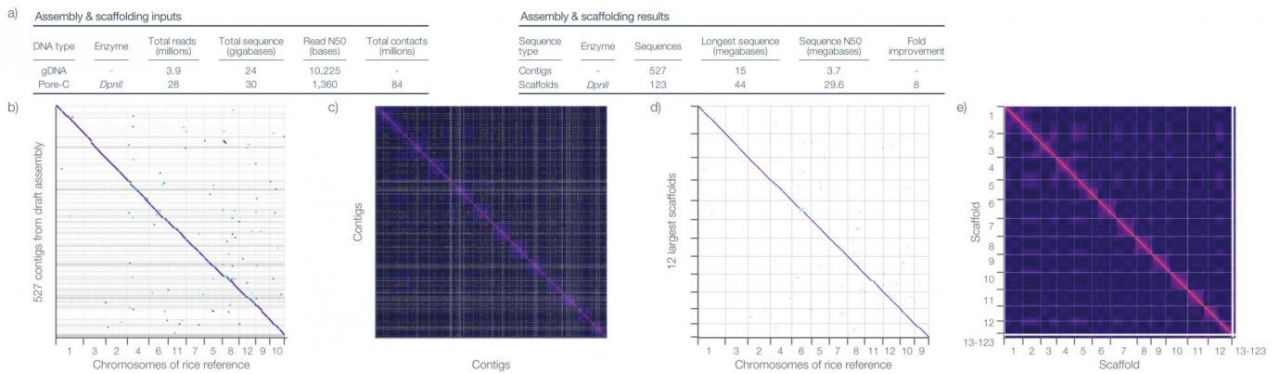
研究者初步组装了水稻Azucena品种基因组,包含527个contigs,contigN50为3.7Mb,并使用30 Gb(~75x)的Pore-C reads进一步增加组装的连续性。组合后的ScaffoldN50≥29.6 Mb(图a)。获得的最大的12个scaffolds接近参考基因组整个染色体的长度。图b c、d e分别显示使用Pore-C数据搭建前后的dot-plot和contact map,图中可知基因组得到明显优化。
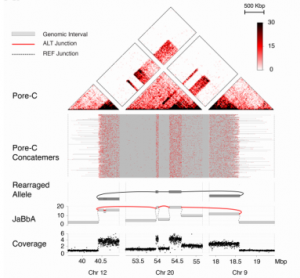
案例二、
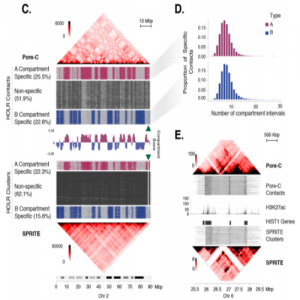
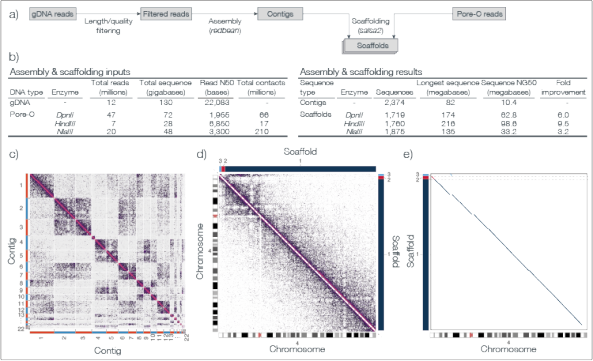
研究者使用130 Gb Nanopore reads组装了人类基因组NA24385,contigN50达到10.4 Mb,并通过使用Pore-C进行scaffolding,进一步提高了人类基因组组装的连续性,使得scaffoldN50高达98.6 Mb。加入Pore-C之前可以看到许多非对角线特征,表明装配不是最佳的(图c, Chr. 4所示)。在Pore-C搭建之后,得到了一个更优的装配,仅三个scaffold变覆盖整条染色体。





 京公网安备 11011302003368号
京公网安备 11011302003368号